Das 3D-Genom des Menschen: ganz anders als das des Schimpansen
Das Genom eines Organismus umfasst die gesamte DNA der Zelle, einschließlich der DNA in den Zellorganellen. Der größte Teil des Genoms von Mensch und Schimpanse (etwa 3 Milliarden Nukleotide A, C, T und G) befindet sich in den Chromosomen im Zellkern. Man stellt sich die Chromosomen normalerweise als lineare Makromoleküle vor, aber im Zellkern sind sie alles andere als linear. Vielmehr bilden sie gezielt 3D-Strukturen, wie z. B. Schleifen, Windungen und Schlingen. Alle bisher untersuchten pflanzlichen und tierischen Genome weisen je nach Zelltyp (z. B. Leber, Lunge, Gehirn, etc.) komplexe und ausgeprägte dreidimensionale (3D) Strukturen in ihren Chromosomenkonfigurationen auf. Die 3D-Konfiguration wird durch Codes bestimmt, die in der DNA oder in mit der DNA assoziierten Proteinen (den sogenannten Histonen) vorhanden sind.

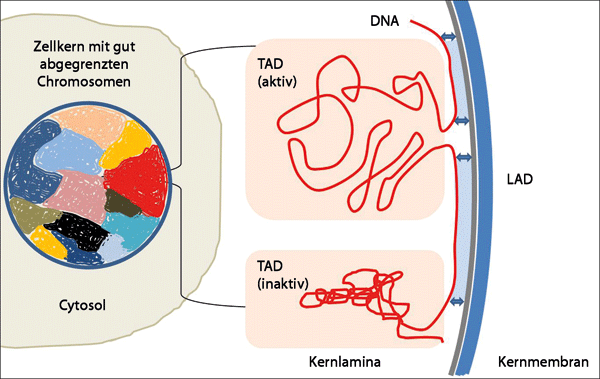
Abb. 1: Neu entdeckte funktionelle Elemente im Genom sind TAD und LAD. TADs sind definiert als Regionen, deren DNA-Sequenzen vorzugsweise miteinander in Kontakt stehen. Lamina-assoziierte Domänen (LADs) sind Teile des Chromatins, die stark mit der Lamina des Zellkerns interagieren. Die Lamina ist ein dichter Verbund von Fibrillen (winzigen Fasern). LADs bilden Langstreckeninteraktionen innerhalb der Chromosomen und sind für die 3D-Konfiguration des Genoms verantwortlich, d. h. sie bestimmen, wie die Chromosomen im Kernraum positioniert sind.
Angesichts der Variabilität der Genomkonfigurationen innerhalb einer einzigen Art von Lebewesen war dieser Bereich der Molekularbiologie für die Evolutionsforschung bisher schwierig. Nun zeigt eine neue Studie, die in der Zeitschrift Trends in Genetics veröffentlicht wurde, dass die menschliche 3D-Konfiguration des Genoms markant und einzigartig für den Menschen ist. Damit werden frühere Forschungen bestätigt, die zeigten, dass sie sich von der 3D-Anordnung des Genoms von Schimpansen genauso deutlich unterscheidet wie von derjenigen von Mäusen (Eres & Gilad 2020).
Eine der besten Möglichkeiten, die 3D-Konfiguration von Chromosomen im Zellkern empirisch zu erfassen, ist die Suche nach sogenannten „topologically associating domains“ (kurz: TADs) in den DNA-Sequenzen des Chromosoms (vgl. Abb. 1). TADs sind DNA-Sequenzen, die in bestimmten Zelltypen bevorzugt miteinander in Kontakt treten und interagieren und mit biologischen Funktionen in Verbindung gebracht werden. Sie sind stark mit sogenannten CCCTC-Bindungsfaktor- (CTCF) und Cohesin-Bindungsstellen angereichert, so dass gut definierte chromosomale Bereiche entstehen – eine Art Plattformen, die zusammenarbeitende Genprogramme miteinander verbinden. Bis vor kurzem konnten TADs nicht untersucht werden, weil es dafür keine geeigneten Technologien gab. Die jüngste Entwicklung von Techniken zur Analyse von Chromosomenkonformationen offenbarte ihre Existenz im Jahr 2012 (Dixon et al. 2012).
Es zeigt sich, dass TADs einen großen Teil der Chromosomen der Eukaryonten (Organismen mit kernhaltigen Zellen) ausmachen. Bei Säugetieren ist die mittlere TAD-Länge etwa 880.000 DNA-Buchstaben (Basen) lang – ein beträchtlicher Abschnitt der DNA, der typischerweise mehrere Gene und viele regulatorische Schalter und Kontrollfunktionen enthält (Yu & Ren 2017). Die 3D-Genomstruktur wird vor allem durch epigenetische Modifikationen (wie Acetylierung oder Phosphorylierung) von Histonen bestimmt, das sind Proteine, um die die DNA gewickelt sind. Diese Modifikationen zeigen nur eine etwa 70-prozentige Ähnlichkeit zwischen Mensch und Schimpanse (Cain et al. 2012). Bemerkenswerterweise zeigte eine andere Studie aus dem Jahr 2012, dass Menschen für dasselbe Merkmal eine Ähnlichkeit von ebenfalls etwa 70 % mit Mäusen aufwiesen (Woo & Li 2012). Mit anderen Worten: Menschen unterschieden sich in Bezug auf diese spezielle Metrik der Genomkonformation genauso sehr von Mäusen wie von Schimpansen.
In der in Trends in Genetics vorgestellten Studie untersuchten die Wissenschaftler nun die TAD-Ähnlichkeit zwischen Menschen und Schimpansen. Sie fanden heraus, dass beim Vergleich von Menschen und Schimpansen „nur 43% der TADs konserviert [= ähnlich] sind“ und „nicht mehr als 78% der Domänen und 83% der TAD-Grenzen von Menschen und Schimpansen geteilt werden“. Dieses unerwartete Ergebnis veranlasste sie zu der Schlussfolgerung: „Unserer Meinung nach gibt es keine solide Grundlage für die verbreitete und oft unbestrittene Vorstellung, dass TADs hoch konserviert sind“ (Eres et al. 2020). Ein Mangel an Konservierung bedeutet hier: unerwartet große Unterschiede, viel zu groß für eine gemeinsame Abstammung.
Diese neue Studie stellt die vermeintliche sehr enge Verwandtschaft zwischen Mensch und Schimpanse weiter in Frage. Sie unterstreicht vielmehr die Einzigartigkeit beider Genome (vgl. Borger 2019). Diese Befunde stehen dagegen in völliger Übereinstimmung mit der Schöpfung, wie sie in dem ersten Buch der Bibel beschrieben wird, wo es heißt, dass Gott die Geschöpfe nach ihrer Art und den Menschen zu seinem Bilde geschaffen hat (1. Mose 1,25–27). Diese tiefgründige Wahrheit wird durch die moderne Genetik immer wieder bestätigt.
P. Borger
[Borger P (2019) Das Erbgut von Mensch und Schimpanse. Stud. Integr. J. 26, 4–10 • Cain CE et al. (2011) Gene Expression Differences Among Primates Are Associated With Changes in a Histone Epigenetic Modification. Genetics 187, 1225–1234 • Dixon JR et al. (2012) Topological domains in mammalian genomes identified by analysis of chromatin interactions. Nature 485, 376–380 • Eres IE & Gilad Y (2020) A TAD Skeptic: Is 3D Genome Topology Conserved? Trends Genet. 37, 216–223 • Yu M & Ren B (2017) The Three-Dimensional Organization of Mammalian Genomes. Ann. Rev. Cell Dev. Biol. 33, 265–289 • Woo YH & Li WH (2012) Evolutionary Conservation of Histone Modifications in Mammals. Mol. Biol. Evol. 29, 1757–1767]