
Themen • Kurzbeiträge • Streiflichter
Sind Pseudogene doch nicht „pseudo“?
Wie ideologisch motivierte Begriffswahl den Fortschritt bremst
von Boris Schmidtgall
Studium Integrale Journal
27. Jahrgang / Heft 1 - Mai 2020
Seite 46 - 50
Zusammenfassung: Pseudogene galten lange Zeit als funktionslos gewordene Gene. Daher wurde über 40 Jahre lang die Suche nach ihren Funktionen im Erbgut von Lebewesen vernachlässigt. Erst im Verlauf der vergangenen 10 Jahre stieg das Interesse an diesen genetischen Elementen – mit dem vielfach bestätigten Ergebnis, dass „Pseudogene“ oft überaus wichtige Funktionen erfüllen. Ein weiteres Mal zeigt sich zweierlei: 1. Die voreilige Aufstellung von Kategorien, ausgehend von der sicher geglaubten Evolutionslehre, ist irreführend. 2. Einordnungen genetischer Elemente als funktionslos gewordene Relikte der Evolution können ein beträchtliches Hindernis für den wissenschaftlichen Fortschritt sein.
• • • • • •

Einführung
Einer der prägnantesten und am meisten zitierten Sätze aus der Bibel steht am Beginn des Johannesevangeliums: „Am Anfang war das Wort …“. Ihre Einprägsamkeit verdankt diese Wendung der untrüglichen Erfahrung eines jeden Menschen, dass vor einem jeden sinnvollen Schaffen ein Gedanke, Plan oder Konzept steht. Solche Dinge werden von Menschen vor dem Schaffensprozess in Worten ausgedrückt – in vergleichbarer Weise, wie dies auch für die Schöpfung gilt, die Gott durch sein Wort hervorbrachte. In diesem Zusammenhang liegt es nicht fern, dass eine genaue Wortwahl eine unverzichtbare Voraussetzung für ein erfolgreiches Schaffen ist. Das gilt ebenso für die Beschreibung bereits vorhandener Naturgegenstände. Dies wird auch als „Aufstellen einer Nomenklatur“ oder als „Schaffen einer Terminologie“ bezeichnet – ein essenzieller Bestandteil der naturwissenschaftlichen Forschung. Besonders wichtig ist hierbei eine große Sorgfalt bei der Wahl von Schlüsselbegriffen, da sie zentrale Stützen eines vermittelten Konzepts sind. Eine lässige oder falsche Begriffswahl zieht hingegen oft ernste Probleme nach sich.
Ein aktuelles Anschauungsbeispiel zu diesem Sachverhalt liefert eine Entwicklung im Bereich der Genetik. Schon in den 1960er- und 1970er-Jahren, als diese junge Wissenschaftsdisziplin noch in den Kinderschuhen steckte, wurden wegweisende Schlüsselbegriffe gewählt, um Sachverhalte zu beschreiben, die sich auf der Ebene der Makromoleküle der Zelle abspielen. Einige Begriffe haben sich bis heute als gut geeignet bewährt. So kann nach wie vor kein Einwand dagegen erhoben werden, dass die DNA ein „Informationsspeicher“ ist und dass bei der Proteinbiosynthese demnach ein „codierter Informationstransfer“ stattfindet. Dazu gehören auch Bezeichnungen wie „Transkription“ (Informationstransfer von der DNA zur RNA) oder „Translation“ (Informationstransfer von RNA zum Protein). Diese zentralen Begriffe haben trotz ihrer schöpfungsfreundlichen Implikationen die Zeit überdauert.
Es wurden damals allerdings auch Begriffe gewählt, die sich mittlerweile als teilweise oder gänzlich unbrauchbar erwiesen haben. Ein besonders auffälliges Beispiel ist der Terminus „junk-DNA“ (Müll-DNA). Dieser Schlüsselbegriff wurde voreilig in der Überzeugung gewählt, dass es sich bei vielen DNA-Abschnitten, für die keine Übersetzung in Proteine nachgewiesen werden konnte, um evolutiven Müll handelt, der sich im Laufe vieler Millionen Jahre angesammelt hat. Doch spätestens seit den wegweisenden Ergebnissen des ENCODE-Projekts hat sich der leichtfertige Umgang mit dem Begriff „junk DNA“ als irrig erwiesen (Pennisi 2012). Gegenwärtig werden solche Kategorisierungen daher zunehmend vorsichtig vorgenommen (Lee 2019).
„Pseudogene“ – Befunde führen zu Umdenken
Mit einem Stern* versehene Begriffe werden im Glossar erklärt.
Ein ähnlich gelagerter Fall ist die Bezeichnung „Pseudogen“. Eingeführt wurde dieser Terminus in einer Publikation, die die nähere Untersuchung bis dahin unbekannter Elemente des Genoms des afrikanischen Krallenfrosches (Xenopus laevis) thematisierte (Jacq et al. 1977). In der betreffenden Arbeit berichten die Autoren über die Entdeckung verkürzter Kopien des 5S-ribosomalen Gens*, für die sie keinen eindeutigen Beleg für die Transkription finden konnten. Daraus schlossen die Forscher a priori1, dass es sich wahrscheinlich um ein evolutionäres Relikt handeln müsse, das keine Funktion hat. Sie bezeichneten dieses Gen daher als „Pseudogen“, was man etwa als „scheinbares Gen“ übersetzen könnte (wörtlich „Lügen-Gen“). Seither steht die Bezeichnung „Pseudogen“ generell für einen für defekt gehaltenen genetischen Abschnitt, der einer funktionalen Gensequenz ähnelt.
Die Forscher schlossen a priori, dass es sich bei dem 5S-ribosomalen Gen um ein evolutionäres Relikt ohne Funktion handeln müsse.
In den letzten zehn Jahren sind allerdings vermehrt Befunde gemacht worden, die ein Umdenken oder zumindest eine differenziertere Betrachtungsweise der „Pseudogene“ nahelegen. Erst kürzlich veröffentlichte die Forschergruppe um Cheetham in der einflussreichen Wissenschaftszeitschrift Nature (2019) zu diesem Thema einen Übersichtsartikel, der an vielen Stellen überraschend offen die Probleme dieser Begriffswahl benennt und analysiert. Schon der Titel „Herausforderungen und Dogmen überwinden, um die Funktionen von Pseudogenen besser zu verstehen“ wirft einige Fragen auf. Gibt es in der Genetik Dogmen, die ein mentales Hindernis für den Fortschritt darstellen? Und wenn ja, woher rühren sie? Wie kann überhaupt noch von „Pseudogenen“ gesprochen werden, wenn es, wie der Titel impliziert, nur darum geht, ihre Funktionen besser zu verstehen? Dass „Pseudogene“ eine ganze Reihe an überaus wichtigen Funktionen ausführen, ist mittlerweile unbestritten. Cheetham und Mitautoren äußern sich dazu wie folgt: „Dort, wo Pseudogene näher untersucht wurden, ist oft nachgewiesen worden, dass sie quantifizierbare biologische Funktionen aufweisen.“ Die Funktionsweisen sind dabei keineswegs von einheitlicher Natur, sondern vielmehr in Abhängigkeit vom jeweiligen Typ des „Pseudogens“ recht verschieden.
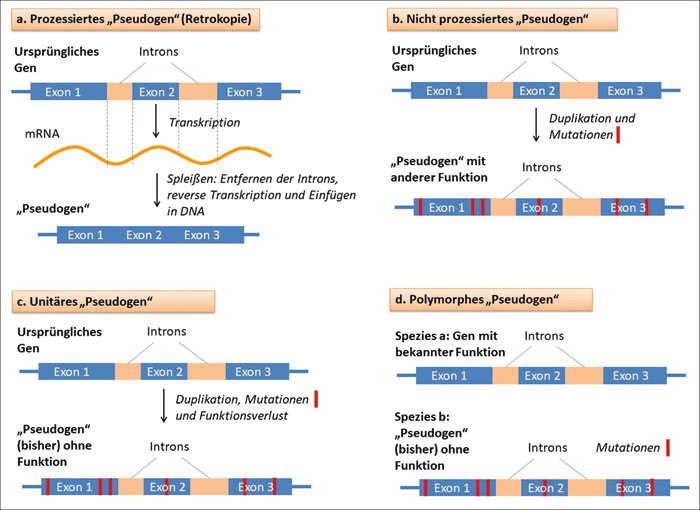
Abb. 1: Bisher übliche Klassifizierung von „Pseudogenen“:
a Prozessierte (verarbeitete) „Pseudogene“ werden auf reverse Transkription aus gespleißter mRNA und nachfolgendes Einfügen in die DNA zurückgeführt. Diese Abschnitte enthalten daher keine Introns.
b Nicht prozessierte „Pseudogene“ sollen durch Duplikation entstanden sein. Durch eine Vielzahl an Mutationen soll ihre Brauchbarkeit für die Proteinbiosynthese verloren gegangen sein.
c Unitäre „Pseudogene“ sollen ebenfalls das Resultat von Duplikationsvorgängen sein, wobei für solche Gene (bisher) keine Funktion bekannt ist. Zudem existiert kein funktionales Duplikat von unitären „Pseudogenen“.
d Polymorphe „Pseudogene“ sind Genabschnitte, die bei einigen Lebewesen eine nachweisbare Funktion ausüben, während sie bei anderen Organismen Mutationen enthalten und (bisher) keine nachweisbare Funktion aufweisen.
Der am häufigsten vorkommende Typ von „Pseudogen“ wird auch als Retrokopie bezeichnet (prozessiertes Pseudogen, Abb. 1a). Das sind genetische Abschnitte, deren Ursprung auf reverse Transkription* aus verarbeiteten (prozessierten) messenger RNA (mRNA) zurückgeführt wird, das heißt aus mRNA, aus der bereits durch den Spleißvorgang* die Introns* entfernt worden sind – die RNA-Transkripte wurden also in DNA zurück übersetzt. Retrokopien innerhalb der DNA werden folglich daran erkannt, dass sie keine Introns enthalten. Einer Schätzung zufolge besteht das menschliche Genom zu 8,9 % aus solchen Abschnitten (Cheetham et al. 2019). Sie stellen bei vielzelligen Lebewesen u. a. wichtige Regulatoren der Virenabwehr und neuronaler Netzwerke* dar. Inzwischen hat es sich erwiesen, dass nicht wenige Retrokopien in Proteine übersetzt werden, womit sie hinsichtlich ihrer Funktion von gewöhnlichen Genen nicht unterscheidbar sind. Ein Beispiel ist das menschliche Gen PGK2, welches für die Synthese eines Enzyms codiert, das spezifisch im Kontext der Spermatogenese* einen Teilschritt der Glykolyse (Zuckerabbau) beschleunigt (Cheetham et al. 2019). Demnach ist in diesem und in ähnlichen Fällen die Bezeichnung „Pseudogen“ eindeutig unzutreffend. In diesem Kontext stellen Cheetham et al. verwundert fest, dass, „obwohl einzelne Retrokopien neu klassifiziert worden sind, viele [andere] intakte Retrokopien weiterhin die Bezeichnung ‚Pseudogen‘ beibehalten.“
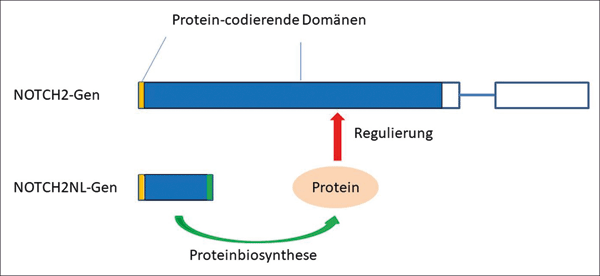
Abb. 2: Qualitativer Vergleich der Strukturen von NOTCH2 und NOTCH2NL. Die grün markierte Domäne von NOTCH2NL unterscheidet sich hinsichtlich der Sequenz deutlich von NOTCH2. NOTCH2NL codiert für ein Protein, welches die Aktivität des NOTCH2-Gens reguliert.
Eine andere Klasse von „Pseudogenen“ stellen genetische Regionen dar, die durch Duplikationen bereits vorhandener Genabschnitte hervorgegangen sein sollen (nicht prozessiertes Pseudogen, Abb. 1b). Häufig sind diese Regionen als „Pseudogene“ bezeichnet worden, weil sie im Vergleich mit dem Original verkürzt sind (wie im o. g. Beispiel von Jacq et al.) oder viele Mutationen aufweisen und daher nicht in Proteine translatiert* werden. Ungeachtet dieser Veränderungen haben auch solche Einheiten oftmals wichtige Funktionen. Ein interessantes Beispiel hierfür ist ein als NOTCH2NL bezeichnetes Human-spezifisches „Pseudogen“. Es weist ein hohes Maß an Ähnlichkeit zum NOTCH2-Gen auf, welches für die Entwicklung des neuronalen Netzwerks in der Großhirnrinde relevant ist. Es konnte nachgewiesen werden, dass das gegenüber NOTCH2 stark verkürzte NOTCH2NL für die Synthese eines Proteins verwendet wird, das durch Wechselwirkung mit NOTCH2 regulatorisch fungiert (Fiddes 2018; Suzuki 2018). Ausgehend von einer evolutionstheoretischen Sichtweise vermuten die Autoren der Studien, dass diese verkürzte Kopie und drei weitere paraloge* Sequenzen nützliche Hinweise auf die Evolution des menschlichen Gehirns sein könnten. Allerdings hat sich gezeigt, dass Veränderungen von NOTCH2NL zu erheblichen Beeinträchtigungen der neuronalen Entwicklung führen können. Deletionen* in diesem Gen sind mit Schizophrenie und Wachstumsstörungen des Gehirns im Embryonalstadium in Verbindung gebracht worden (Fiddes 2018). Eine erhöhte Anzahl an NOTCH2NL-Kopien steht im Verdacht, Autismus auszulösen (Fiddes 2018). Es sieht also nicht danach aus, als sei dieses Gen eine Art „Spielwiese der Evolution“, wie oft in Bezug auf duplizierte Gene vermutet wird.
Ein weiteres besonders beeindruckendes Beispiel eines „Pseudogens“ stellt das HBB1-Gen dar, welches sich als cis-regulatorisches* Element in Bezug auf den kurz vor der Geburt einsetzenden Umstellungsvorgang von fetalem Hämoglobin auf adultes erwiesen hat (Huang et al. 2017). Die Ähnlichkeit dieser „Pseudogene“ bei Mensch und Schimpanse wurde lange Zeit als Argument für deren gemeinsame Abstammung angeführt (Chang & Slightom 1984). Mit der Entdeckung der funktionalen Relevanz dieser Gene wird diese Argumentation allerdings hinfällig, da ihre Interpretation als evolutionäres Relikt nicht mehr schlüssig ist (Anderson 2011).
Zur Kategorie der „Pseudogene“ werden auch genetische Einheiten gezählt, die nicht aus Duplikationen hervorgegangen sind und bei denen es durch Mutationen zu einem Funktionsverlust gekommen sein soll (unitäre Pseudogene, Abb. 1c). Solche Gene werden als „unitär“ bezeichnet, da keine entsprechende intakte Kopie vorhanden ist. In einigen Fällen wurden durch Mutationen funktionsunfähig gewordene genetische Abschnitte zu den „Pseudogenen“ gezählt, die bei anderen Lebewesen nachweislich eine Funktion haben (polymorphe Pseudogene, Abb. 1d). Unitäre „Pseudogene“ und solche, die durch Mutationen eine bei anderen Lebewesen beobachtete Funktion vermutlich verloren haben, sind deutlich seltener als die weiter oben angesprochenen Retrokopien und verkürzte Genkopien. Auf diese Minderheit soll im Folgenden nicht weiter eingegangen werden.
Wie bereits erwähnt, sind die bisher entdeckten Funktionsweisen von als „Pseudogenen“ bezeichneten Genabschnitten vielfältig. Neben den bereits erwähnten Protein-codierenden „Pseudogenen“ (Protein-basierte Funktion) sind vor allem solche gefunden worden, die regulatorisch aktiv sind. Einige „Pseudogene“ nehmen Einfluss auf die Proteinbiosynthese, indem sie die Struktur des Chromatins* durch Kontakt verändern (DNA-basierte Funktion), andere dienen zwar nicht als Informationsquellen für die Synthese von Proteinen, werden aber in RNA-Moleküle transkribiert (umgeschrieben), die anschließend regulatorisch in die Proteinbiosynthese eingreifen (RNA-basierte Funktion). Dazu zählen z. B. microRNA oder small interferingRNA, die durch Aktivierung des Proteinkomplexes RISC (RNA induced silencing complex) die Zersetzung bestimmter mRNA-Moleküle auf dem Weg vom Zellkern zum Ribosom katalysieren* (Grishok et al. 2001). Auf diese Weise können Gene stillgelegt werden, obwohl sie transkribiert werden.
Glossar
Chromatin: kompakt angeordneter Komplex aus DNA und bestimmten Proteinen (Histonen). cis-regulatorisches Element: Das „cis“ steht für „diesseits“. Es handelt sich um Abschnitte der DNA, die eine regulatorische Funktion aufweisen, ohne vorher in RNA oder Proteine umgeschrieben worden zu sein. Diese Abschnitte wirken direkt, z. B. durch Wechselwirkung mit anderen Abschnitten der DNA. Deletion: Verlust. Liegt vor, wenn in einer DNA-Sequenz ein einzelnes oder mehrere DNA-Bausteine im Vergleich zu einer ansonsten identischen anderen DNA-Sequenz fehlen. Exon: → Spleißvorgang. Intron: → Spleißvorgang. katalysieren: eine chemische Reaktion beschleunigen. 5S-ribosomales Gen: Gen, das für eine Komponente codiert, die die Struktur des Ribosoms stabilisiert und so die Proteinsynthese verbessert. neuronales Netzwerk: aus Nervenzellen bestehendes Netzwerk. paraloge Gene (Sequenzen): Durch Duplikation entstandene Gene oder Genabschnitte, die hinsichtlich ihrer Sequenz sehr ähnlich sind. reverse Transkription: Synthese von DNA-Molekülen ausgehend von RNA-Vorläufern durch das Enzym Reverse Transkriptase. Dieser Vorgang stellt eine wichtige Ausnahme zum sog. zentralen Dogma der Molekularbiologie dar, dem zufolge der Informationsfluss nach dem Schema DNA → RNA → Protein verläuft. Spermatogenese: Erzeugung von Spermien. Spleißvorgang: Ein Prozess, bei dem das mRNA-Molekül nach erfolgter → Transkription am Spleißosom (großer Proteinkomplex) verarbeitet wird. Hierbei werden aus der mRNA bestimmte Segmente (Introns) ausgeschnitten und entfernt, während die restlichen Segmente (Exons) zu einer neuen mRNA zusammengefügt werden. Dieses reife mRNA-Molekül gelangt anschließend zum Ribosom und wird zur Proteinsynthese verwendet. Transkription: Umschreiben von DNA in mRNA (messenger RNA). Translation (auch translatiert): Synthese der RNA ausgehend von der DNA durch das Enzym Transkriptase.
Ursachen und Folgen der ungeeigneten Begriffswahl „Pseudogen“
Angesichts der wachsenden Zahl an mittlerweile entdeckten Funktionen der vormals für funktionslos gehaltenen „Pseudogene“ stellt sich die Frage: Weshalb hat es so lange gedauert, bis die Funktionen der Pseudogene ans Licht kamen? Denn seit der Entdeckung verkürzter Genkopien bis zur aktuell anschwellenden Welle an Veröffentlichungen zu „Pseudogenen“ sind über 40 Jahre vergangen. Die Autoren um Cheetham geben hierfür folgende Erklärung: „Wir sind der Auffassung, dass ein ausgeprägtes Missverstehen von Pseudogenen, welches teilweise durch die abwertende Schlussfolgerung aus dem Begriff ‚Pseudogen‘ aufrechterhalten wurde, dazu geführt hat, dass sie [die Pseudogene] häufig von Beurteilungen bezüglich einer Funktion und von Genomanalysen ausgeschlossen wurden.“ An anderer Stelle fügen die Autoren hinzu: „Wir […] beschreiben, wie methodologische Einschränkungen und größtenteils willkürlich getroffene Annahmen die Erforschung von als Pseudogen bezeichneten Genregionen behinderten.“
Der Begriff „Pseudogen“ stellte ein mentales Hindernis dar, das den Erkenntnisfortschritt im Bereich der Genetik eingeschränkt hat.
Es ist also offenkundig, dass die ungeeignete Begriffswahl im Hinblick auf bestimmte Elemente des Genoms von Lebewesen dazu geführt hat, dass sie über mehrere Jahrzehnte in der Forschung unberücksichtigt blieben. Darüber hinaus bestätigen Cheetham et al., dass diese Begriffswahl wohl auch die Entwicklung von Schlüsseltechnologien zur Erforschung von „Pseudogenen“ gehemmt hat: „Zusätzlich zu der Demotivation, die Funktion von Pseudogenen zu erforschen, die von der a-priori-Annahme ihrer Funktionslosigkeit herrührte, wurde ihre systematische Erforschung durch einen Mangel an soliden Technologien behindert, die es ermöglicht hätten, biologische Aktivitäten der Pseudogene von denjenigen [gewöhnlicher Gene] zu unterscheiden, von denen sie abgeleitet werden.“ Dass es technisch schwierig ist, diese Genregionen zu erforschen, liegt offensichtlich daran, dass die Entwicklung von Technologien hauptsächlich auf die Identifikation und Untersuchung proteincodierender Genregionen fokussiert war. Es wird also deutlich, dass der Begriff „Pseudogen“ tatsächlich ein mentales Hindernis darstellte, das zu einem nicht unerheblichen Ausmaß den Erkenntnisfortschritt im Bereich der Genetik eingeschränkt hat.
Was der Artikel von Cheetham et al. nicht klar zur Sprache bringt
Den Autoren um Cheetham ist es hoch anzurechnen, dass sie den Mut aufgebracht haben, ein herrschendes Paradigma infrage zu stellen, das aufgrund von neuen Befunden zunehmend an Legitimation verliert. Sie geben darüber hinaus offen zu, dass das Pseudogen-Paradigma willkürlich gesetzt worden ist: „Zusätzlich zu der ungeprüften Hypothese, dass die Evolution uns mit einer Gegensätzlichkeit von Genen und Pseudogenen zurückgelassen hat, stellt der Begriff ‚Pseudogen‘ durch seine taxonomische Konstruktion ein Paradigma der Nichtfunktionalität auf.“ Ferner ist Cheetham et al. uneingeschränkt zuzustimmen, dass „[…] es ein übergeordnetes Prinzip sein sollte, dass die Terminologie dem Endverbraucher keine unbegründete Annahme aufzwingen sollte.“
Der irreführende Terminus „Pseudogen“ und das dazugehörige Konzept beruhen auf der Evolutionslehre.
Allerdings genügt es nicht, die Ursache für die Einschränkung des Fortschritts allein bei einem Schlüsselbegriff zu suchen, denn das eigentliche Problem liegt in dem Konzept, welches hinter dem Begriff steht. Schließlich beruht das Denken, welches dazu geführt hat, dass der irreführende Terminus „Pseudogen“ und das dazu gehörige Konzept sich in der wissenschaftlichen Literatur etabliert haben, auf der Evolutionslehre, wie die eingangs geschilderte Entstehungsgeschichte des Begriffs verdeutlicht. An keiner Stelle im Artikel von Cheetham et al. wird kritisch reflektiert, dass dieser unmittelbare Zusammenhang besteht und letztlich die tiefere Ursache der bedauerlichen Fehlentwicklung von Teilen einer Wissenschaftsdisziplin ist. Die Kritik von Cheetham et al. verlässt nicht den ebenfalls willkürlich gesetzten Rahmen der evolutionistischen Weltanschauung, obwohl das Pseudogen-Konzept sich zunehmend offenkundig zu den gescheiterten evolutionstheoretischen Argumentationsmustern wie der evolutionären Flickschusterei (z. B. Linsenauge) oder der Dichotomie von Homologie und Konvergenz gesellt. Es ist daher leicht vorherzusehen, dass sich vergleichbare Szenarien künftig wiederholen werden. Schließlich ist das Scheitern des Pseudogen-Konzepts schon vor einiger Zeit von Forschern, die die Schöpfungslehre befürworten, vorhergesagt worden (Woodmorappe 2003; Wells 2011).
1 Hier kann natürlich der Einwand erfolgen, dass der Schluss nicht a priori erfolgte, da das „Pseudogen“ ja erst als solches bezeichnet wurde, nachdem alle Untersuchungen auf Transkription keine positiven Belege ergaben. Dennoch war die Bezeichnung als „evolutionäres Relikt“ ohne Funktion eine a-priori-Festlegung, da bei weitem nicht alle funktionalen Möglichkeiten untersucht worden waren.
Shared Mutations in the human and chimpanzee b-globin pseudogenes is not evidence for creation. J. Creation 25, 10–12.
Isolation and nucleotide sequence analysis of the ß-type globin pseudogene from human, gorilla and chimpanzee. J. Mol. Biol. 180, 767–784.
Overcoming challenges and dogmas to understand the functions of pseudogenes. Nat. Rev. Genet. 1–11, doi:10.1038/s41576-019-0196-1.
Human-specific NOTCH2NL genes affect Notch signaling and cortical neurogenesis.Cell 173, 1356–1369.
Genes and mechanisms related to RNA interference regulate expression of the small temporal RNAs that control C. elegans developmental timing. Cell 106, 23–34.
Comparative analysis of three-dimensional chromosomal architecture identifies a novel fetal hemoglobin regulatory element. Gen. Dev. 31, 1704–1713.
A pseudogene structure in 5S DNA structure of Xenopus laevis. Cell 12, 109–120.
Long noncoding RNA and repetitive elements: junk or intimate evolutionary partners? Trends in Genetics 35, 892–902.
ENCODE Project writes eulogy for junk DNA. Science 337, 1159–1161.
Human-specific NOTCH2NL genes expand cortical neurogenesis trough delta/notch regulation. Cell 173, 1370–1384.
The myth of junk DNA. Discovery Institute Press, p47–55.
Pseudogene function: regulation of gene expression, J. Creation 17, 47–52.
Themen | Kurzbeiträge | Streiflichter
Studiengemeinschaft WORT und WISSEN e.V.
Letzte Änderung: 6/21/21
Webmaster