Themen • Kurzbeiträge • Streiflichter
Dreidimensionale Informationsebene der DNA entdeckt
von Boris Schmidtgall
Studium Integrale Journal
27. Jahrgang / Heft 1 - Mai 2020
Seite 51 - 53
Zusammenfassung: In der Vergangenheit wurden weite Teile im Erbgut der Lebewesen als „junk-DNA“ gewertet, d. h. als funktionslose genetische Einheiten, die Spuren einer lange zurückliegenden Evolution sein sollen. Für diese genetischen Regionen werden jedoch zunehmend wichtige Funktionen gefunden. Dies gilt auch für DNA-Sequenzen mit häufig sich wiederholendem Strukturmotiv: die Isochoren. Der Molekularbiologe Bernardi zeigt in einer aktuellen Veröffentlichung, dass es sich um genetische Elemente handelt, die die Information für die korrekte räumliche Anordnung der DNA im Zellkern speichern.
• • • • • •
Einführung
Zweifelsohne ist das Erbmaterial aller Lebewesen, die DNA, eines der faszinierendsten Moleküle überhaupt. Nicht lange nach der Charakterisierung ihrer dreidimensionalen Helix-Struktur (1953) soll James Watson gesagt haben: „Ich glaube, nur wenige Entdeckungen waren von so perfekter Schönheit.“ Wie es scheint, haben sich die Überraschungsmomente im Zusammenhang mit der Untersuchung der DNA auch bis heute nicht erschöpft – nach knapp 70 Jahren intensiver Forschung. Nachdem in den 1960er- und 1970er-Jahren der genetische Code entschlüsselt und die Verpackung der DNA charakterisiert wurde, wurde von einigen einflussreichen Experten die Auffassung verbreitet, dass nur die ca. 2 % proteincodierenden DNA-Sequenzen funktional seien. Die restlichen 98 % wurden ausgehend von der Evolutionslehre als „junk-DNA“ tituliert, d. h. als im Zuge vieler Jahrmillionen des evolutiven Wandels funktionsunfähig gewordener genetischer Abfall (Ohno 1972). Allerdings ist diese Auffassung im Verlauf der vergangenen 20 Jahre zunehmend in die Kritik geraten, da eine Vielzahl an Befunden dafür spricht, dass mindestens 80 % des menschlichen Genoms funktional sind (ENCODE 2012). Der wesentliche Irrtum der junk-DNA-Hypothese bestand in der voreiligen Annahme, dass genetische Abschnitte, die nicht für die Synthese von Proteinen verwendet werden, gar keiner Funktion dienen. Es wurde nämlich vermehrt herausgefunden, dass die früher für funktionslos gehaltenen Gensequenzen vor allem regulatorische Funktionen ausüben. Der häufig in diesem Kontext verwendete Begriff „Pseudogen“ hat sich daher oft als unzutreffend erwiesen (Schmidtgall 2020). Auch Introns, die früher für evolutionäre Überbleibsel gehalten wurden, haben sich bei näherer Untersuchung als funktional erwiesen (Parenteau et al. 2019).

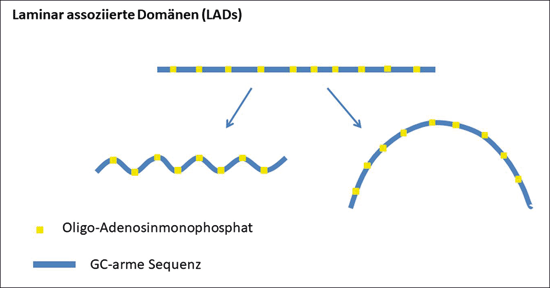
Abb. 1: Schematische Darstellung der Strukturmotive von laminar assoziierten Domänen (LADs). Es handelt sich dabei um GC-arme genetische Regionen, die mit Oligo-Adenosinmonophosphat-Einheiten bestückt sind, d. h. Serien von mehreren aufeinander folgenden Adenosinmonophosphat-Bausteinen enthalten. Diese Einheiten bewirken lokale Kurven- oder Bogenstrukturen in der DNA. Isochoren*: von „Müll-DNA“ zu unverzichtbaren DNA-Abschnitten
Mit einem Stern* versehene Begriffe werden im Glossar erklärt.
Eine andere Klasse von genetischen Abschnitten, die lange Zeit ebenfalls der Kategorie „junk-DNA“ zugeordnet wurden, sind die Isochoren1. Dies sind lange repetitive (ein häufig sich wiederholendes Strukturmotiv enthaltende) DNA-Abschnitte, die bis jetzt vor allem für Relikte von Viren gehalten wurden (Palazzo & Gregory 2014). Doch kürzlich berichtete der italienische Molekularbiologe Giorgio Bernardi in einem Übersichtsartikel darüber, dass die Isochoren offenbar sehr wichtige Funktionen für die gesamte Zelle ausüben (Bernardi 2019). Demnach wurde über diese DNA-Untereinheiten herausgefunden, „[…] dass diese Strukturen, die wesentlich auf der Verteilung und Topologie* kurzer DNA-Sequenzen basieren, primäre Chromatin*-Domänen* formen und die Bindungsweise von Nucleosomen* definieren“. Vereinfacht ausgedrückt heißt das, dass die Isochoren, je nachdem wie sie strukturell beschaffen sind, einen erheblichen Einfluss auf die Struktur der Verpackung der DNA im Zellkern ausüben. Bernardi spricht in diesem Zusammenhang von einem „genomischen Code“ – also einer codierten Information darüber, wie die DNA im Zellkern dreidimensional angeordnet werden soll: „Zudem ist der genomische Code allgegenwärtig im Genom und löst daher alte herausragende Probleme wie ‚nicht-codierende DNA‘, junk-DNA‘ oder ‚egoistische DNA‘“. Demnach ist der Effekt der Isochoren keinesfalls lokal begrenzt, sondern betrifft die gesamte Struktur der Erbmoleküle im Zellkern.
Die Isochoren weisen keine einheitlichen Zusammensetzungen auf und werden daher in fünf Untergruppen eingeteilt (L1, L2, H1, H2, H3). Entscheidend für die Einteilung in die Untergruppen der Isochoren ist der Gehalt an GC-Basenpaaren (G = Guanin, C = Cytosin). In den zwei Unterklassen L1 und L2 sind GC-arme* Isochore eingegliedert. Diese genetischen Regionen sind arm an exprimierten* Abschnitten („Gen-Wüsten“) und befinden sich hauptsächlich an der Innenseite der Zellwand des Zellkerns. Sie stellen eine Art Verankerung des Chromatins an der Zellwand des Zellkerns dar (Lochs 2019). Diese Verankerung wird als laminar assoziierte Domäne (LAD) bezeichnet und fördert die korrekte räumliche Anordnung des Chromatins im Zellkern (Abb. 1). Einen deutlich höheren GC-Gehalt weisen die Isochoren der Klassen H2 und H3 auf. Sie ragen ins Innere des Zellkerns, wo sie durch gegenseitige Wechselwirkungen die Struktur der topologisch* assoziierten Domänen (TAD) formen – eine Funktion, die das Chromatin in der richtigen dreidimensionalen Form hält. Darüber hinaus beinhalten die GC-reichen Isochoren deutlich mehr proteincodierende Abschnitte als die GC-armen Abschnitte der Klassen L1 und L2. Details der Funktionsweisen von LAD und TAD sind noch nicht gründlich untersucht, aber es ist bekannt, dass Veränderungen dieser Strukturen schwere Erkrankungen hervorrufen können (z. B. Krebs) (Lochs 2019).
Glossar
Chromatin: kompakt angeordneter Komplex aus DNA und bestimmten Proteinen (Histonen). Domäne: Bestimmter Bereich/Abschnitt im Erbgut. exprimieren: „ausprägen“; Synthetisieren von Proteinen am Ribosom, ausgehend von der Information der DNA. GC-arme DNA-Sequenzen: DNA-Sequenzen, die nur wenige G-C(Guanosin-Cytosin)-Basenpaare enthalten. Isochore: Lange DNA-Sequenz mit häufig sich wiederholendem Strukturmotiv. Nucleosomen: Kugelförmige Art der DNA-Verpackung mit Proteinen. Topologie: Dreidimensionale Anordnung bestimmter Objekte im Raum.
Weiterer Hinweis auf mehrschichtige Informationsspeicherung
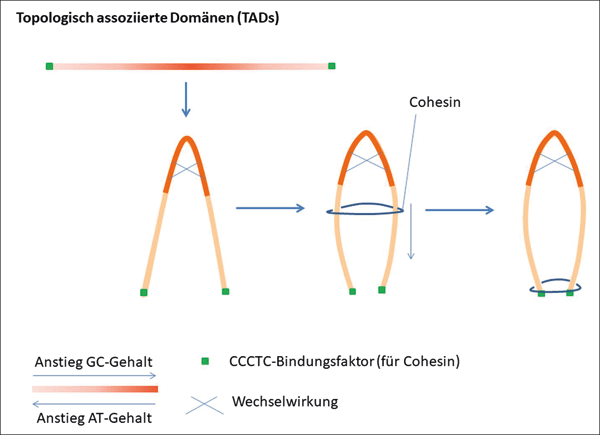
Abb. 2: Modell der Faltung von TADs: Durch interne Wechselwirkungen in der GC-reichen Region wird zunächst eine Schleifen-Struktur geformt. Anschließend wird diese Anordnung durch ein Cohesin (ringförmiges Protein) weiter befestigt. Das Cohesin gleitet von der GC-reichen Region bis zum CCCTC-Bindungsfaktor, wo es schließlich bindet.
Der Umstand, dass dieselben DNA-Sequenzen sowohl Proteine codieren als auch eine genomische Codierung enthalten können, bedeutet eine Überlappung zweier Informationsebenen. Hier ist also eine hohe Informationsdichte sehr effizient verwirklicht worden. Dabei ist das Vorliegen mehrerer überlappender Informationsebenen auf der DNA schon in anderen Zusammenhängen erkannt worden. Ein anderes Beispiel sind intrinsisch unstrukturierte Proteine, die mehrere spezifische Faltungen annehmen können – eine Eigenschaft, die entsprechende mehrschichtige Informationsspeicherung auf der Erbsubstanz voraussetzt (Schmidtgall 2018). Die überaus hohe Informationsdichte auf der DNA ist ein sehr belastbares Design-Indiz.
Dieselben DNA-Sequenzen codieren sowohl Proteine als auch die räumliche Anordnung der DNA. Diese Überlappung zweier Informa-tionsebenen ist ein sehr belastbares Design-Indiz.
Mit den Isochoren lässt sich darüber hinaus noch ein anderer Sachverhalt sinnvoll erklären: Die Variabilität der dritten Position von DNA-Codons. Dies soll anhand eines Beispiels erläutert werden: Die Aminosäure Arginin wird durch die Nucleotid-Kombinationen CGT, CGC, CGA, CGG codiert, d. h. die dritte Position ist hier redundant. Ausgehend von der Evolutionslehre wurde vermutet, dass die letzte, variable Position unwichtig sei und eine Art Hinweis auf die ungerichteten Naturkräfte, die den genetischen Code hervorgebracht haben sollen. Doch mit dem Wissen um den genomischen Code wird deutlich, dass die letzte Position offenbar dazu da ist, den genomischen Code zu speichern – parallel zur Codierung der Struktur von Proteinen. So kann zwar die gleiche Aminosäure in unterschiedlichen genetischen Abschnitten codiert sein, aber die letzte Position kann durch die Wahl von A/T oder G/C darüber bestimmen, ob es sich bei dem genetischen Abschnitt um eine im LAD fungierende Einheit handelt oder um eine Sequenz, die am TAD wirksam ist.
Widersprüchliches Festhalten am evolutionären Bekenntnis
Bernardi folgert an mehreren Stellen in seinem Übersichtsartikel, dass mit der Entdeckung des „genomischen Codes“ das evolutionäre Konzept „junk DNA“ sehr fraglich wird. Allerdings versucht er dennoch, den Ursprung der genetischen Information auf Evolution zurückzuführen: „Am Ende der 1980er-Jahre hat uns das Wissen um die Organisation der Isochoren im menschlichen Genom dazu gebracht, die Vorstellung zu verwerfen, die DNA sei gewissermaßen ein ‚Erbsenbeutel‘, also eine Ansammlung von Genen, die zufällig über große Bereiche von Müll-DNA verstreut waren. Es konnte aber auch gezeigt werden, dass das Genom ein integriertes, strukturiertes, funktionales und evolutionäres System ist.“2
Es ist gezwungen und unpassend, das Erbgut-System als „evolutionär“ zu bezeichnen, da es wesentliche Merkmale des Geschaffenseins trägt.
Der zitierte Satz wirkt an sich durchaus schlüssig, bis das Wort „evolutionär“ eingefügt wird. In diesem Satz ist dieses Wort aber völlig überflüssig. Der Begriff „evolutionär“ ergibt sich hier nicht sinnvoll aus dem vorher Gesagten, sondern stellt lediglich ein weltanschauliches Bekenntnis des Autors da. Angesichts der beschriebenen Befunde ist es jedoch gezwungen und unpassend, das System als „evolutionär“ zu bezeichnen. Denn wie soll ein System zugleich wesentliche Merkmale eines geschaffenen Gegenstandes aufweisen (integriert, strukturiert, funktional) und dennoch aus ungerichteten Naturvorgängen hervorgegangen sein? Diese Gegensätzlichkeit tritt besonders oft im Zusammenhang mit Entdeckungen aus dem Bereich der Molekularbiologie auf und wird in keinem Fall aufgelöst. Das liegt möglicherweise daran, dass kaum ein Fachgebiet so deutliche Indizien für Schöpfung liefert wie die Molekularbiologie bzw. Genetik. Daher kann die evolutionäre Weltsicht in diesem Kontext nur durch rhetorische Verschleierung aufrechterhalten werden.
Es bleibt zu hoffen, dass sich künftig Wissenschaftler finden, die aufrichtig und mutig genug sind, dem ideologischen Diktat der Bildungs- und Medieneinrichtungen nicht zu folgen und auf Bekenntnisse zum Naturalismus zu verzichten, um sich auf die Befunde und die daraus sich zwingend ergebenden Schlussfolgerungen zu fokussieren.
1 Von griech. isos = gleich, chorodia = Fülle, Volumen, diese Bezeichnung wurde aufgrund der global ähnlichen Zusammensetzung der Abschnitte aus den vier genetischen Bausteinen A, C, G, T vergeben.
2 „By the end of the 1980s, our knowledge of the isochore organization of the human genome had not only rejected what had been called the ‚bean-bag‘ view of the genome, that is, a collection of genes randomly scattered over vast expanses of ‚junk DNA‘; but it had also indicated that the genome is an integrated structural, functional, and evolutionary system.“
The genomic code: a pervasive coding/molding of chromatin structures. BioEssays 41, 1900106.
Lamina Associated Domains and Gene Regulation in Development and Cancer. Cells 8, doi:10.3390/cells8030271.
So much ‘‘junk’’ DNA in our genome. In: Smith HH (ed) Evolution of genetic systems. New York: Gordon and Breach, pp 366–370.
The case for junk DNA. PLoS Genetics 10, e1004351.
Introns are mediators of cell response to starvation, Nature, doi: 10.1038/s41586-018-0859-7.
Intrinsisch unstrukturierte Proteine. Stud. Integr. J. 25, 84–91.
Sind Pseudogene doch nicht pseudo? Wie ideologisch motivierte Begriffswahl den Fortschritt bremst. Stud. Integr. J. 27, 46–50.
Themen | Kurzbeiträge | Streiflichter
Studiengemeinschaft WORT und WISSEN e.V.
Letzte Änderung: 6/21/21
Webmaster