Neue micro-RNA-Gene bei Menschen widerlegen lang gehegte evolutionäre Überzeugung
Downloads
Eine insbesondere seit Darwin verbreitete Ansicht lautet: „Die Natur macht keine Sprünge.“ Mit Hilfe neuartiger hochempfindlicher Genomforschungsinstrumente scheint diese Ansicht als falsch erwiesen worden zu sein, denn die Genome aller Organismen enthalten eine beträchtliche Anzahl sogenannter Waisengene (engl. orphan genes). Jede untersuchte Gattung hat 10–30 % solcher de-novo-Gene, also Gene, für die keine Evolutionsgeschichte ermittelt werden konnte. Bei diesen Genen kann es sich um proteincodierende Gene, nicht-codierende RNA-Gene und micro-RNA-Gene handeln. Nach einer neuen Studie können micro-RNA-Gene durch ein einziges genetisches Ereignis, das so genannte Template Switching, entstehen.
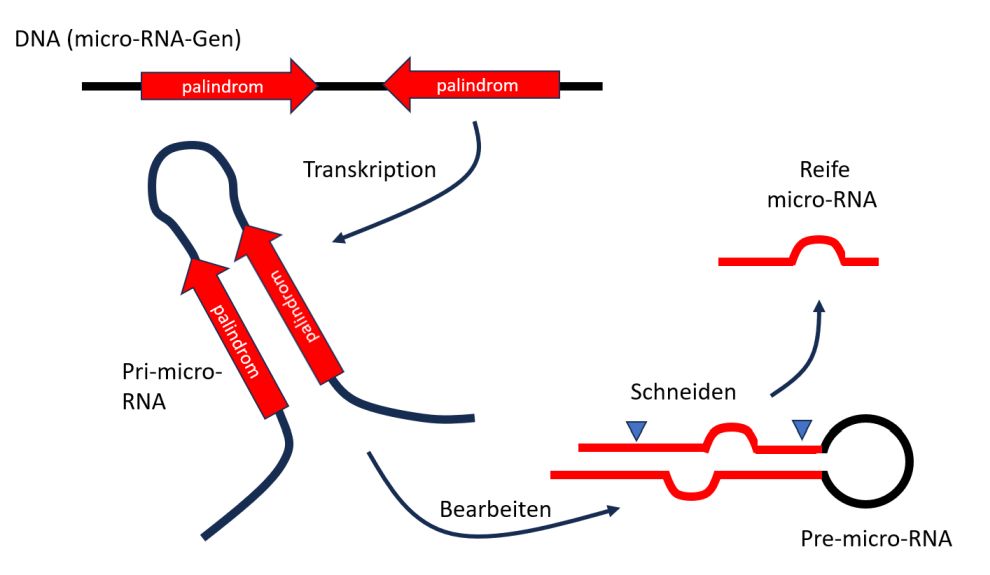
Abb. 1 (Introbild) Micro-RNA-Gene befinden sich in der DNA. Sie werden in pri-micro-RNAs umgeschrieben, die enzymatisch zu pre-micro-RNAs verarbeitet werden. Diese wiederum werden enzymatisch zu reifen micro-RNAs von etwa 22 Nukleotiden verarbeitet. Reife micro-RNAs kontrollieren die Expression ganzer biologischer Netzwerke, da sie bis zu mehreren hundert Messenger-RNAs binden und deren Abbau bewirken können.
Micro-RNA
Das erste micro-RNA-Gen wurde 1993 völlig unerwartet im Genom des Spulwurms (Caenorhabditis elegans) entdeckt. Anfangs hielt man dies für einen Einzelfall, also etwas, das nirgendwo sonst in der Natur vorkommt. Als die Biologen aber anfingen, gezielt nach micro-RNA-Genen zu suchen, wurden sie in allen Tier- und Pflanzengruppen fündig, bei Schwämmen, Rädertierchen, Pflanzen, Insekten und Säugern (Fromm et al. 2015). Micro-RNA-Gene werden nicht in Proteine umgeschrieben. Stattdessen codieren sie für kurze RNA-Moleküle, die regulatorische Funktionen erfüllen. Bei micro-RNA handelt es sich um kleine RNA-Moleküle, die üblicherweise nur aus 22 Nukleotiden (RNA-Bausteine) bestehen und die messenger-RNA (mRNA) von proteincodierenden Genen erkennen und an diese binden. Auf diese Weise blockieren sie entweder die Übersetzung der mRNA in Proteine oder markieren die mRNA für die Abbaumaschinerie, damit von dem entsprechenden Protein weniger produziert werden kann. In beiden Fällen kommt es zu einer verminderten Produktion des betreffenden Proteins. In der Regel erkennt jede einzelne micro-RNA Hunderte von verschiedenen mRNAs, wodurch die Aktivität von umfangreichen genetischen Programmen gesteuert werden kann. Der Protein-Output von etwa 60 Prozent aller menschlichen Gene wird durch micro-RNAs gesteuert. Micro-RNAs werden auf verschiedene Weise produziert, aber in der Regel werden sie von bestimmten Genen codiert (O‘Brien et al. 2018).
Ein micro-RNA-Gen hat eine leicht erkennbare Struktur, da innerhalb der entsprechenden DNA-Sequenz ein Palindrom vorhanden ist. Ein Palindrom (wie das Wort „Lagerregal“; das Wort kann vorwärts und rückwärts gelesen werden) besteht aus zwei eng beieinander liegenden, benachbarten invertierten Wiederholungen, die intern miteinander durch Basenpaarung eine Haarnadel-Struktur (oder Stammschleife) bilden (Abb. 1). Palindrome in der DNA sind keine Seltenheit und haben oft wichtige biologische Funktionen, da die Schleifen, die sie in DNA-Sequenzen verursachen, oft als Andockstellen für regulatorische Proteine dienen. Gene, die für micro-RNA-Moleküle codieren, sind genauso Bestandteile des menschlichen Genoms wie Gene, die für Proteine codieren. Zellen stellen micro-RNA in einem Prozess her, der den ersten Schritten der Proteinsynthese ähnelt. Das micro-RNA-Gen wird aktiviert, indem der DNA-Strang von einer Transkriptase (Enzym) geöffnet wird. Anschließend wird das Gen in RNA umgeschrieben (Transkription).
Beim Menschen gibt es 94 einzigartige micro -RNA-Gene „ohne Evolutionsgeschichte“.
Es ist immer noch unklar, wie viele micro-RNA-Gene im menschlichen Genom vorhanden sind. Verschiedene Datenbanken geben eine unterschiedliche Anzahl von micro-RNA-Genen an, bis hin zu mehreren Tausend. Jüngste Analysen mit modernsten Techniken bestätigen 567 micro-RNA-Gene im menschlichen Genom, von denen 94 nur beim Menschen vorkommen (https://mirgenedb.org/browse/hsa , am 25.01.2024). Bei Letzteren handelt es sich also um sogenannte Orphan-Gene (Waisengene), d. h. Gene, die nur bei einer bestimmten Art vorkommen und bei denen es keine Hinweise gibt, wie sie im Sinne einer evolutionären Entwicklungsgeschichte interpretiert werden könnten. Dies ist für Evolutionstheoretiker sehr problematisch, denn woher kommen neue Gene, die keine evolutionäre Geschichte haben? In einem kürzlich in der US-amerikanischen Wissenschaftszeitschrift PNAS erschienenen Artikel wird postuliert, dass sie in einem Mutationsprozess namens „Template Switching“ gebildet werden können, der gelegentlich während der DNA-Replikation auftritt (Mönttinen et al. 2023).
Was ist „Template Switching “?
Template Switching (TS; deutsch: Vorlagenwechsel) wird häufig zur Erklärung der Bildung komplexer neuer Haarnadelstrukturen in Genomen herangezogen (Mönttinen et al. 2022). Um zu verstehen, was mit TS gemeint ist, kann man sich die doppelsträngige DNA wie eine zweispurige Straße vorstellen, die in beide Richtungen befahren werden kann – aber immer und nur auf der rechten Seite befahren werden darf, wie es die StVO fordert. Bei der Replikation* der DNA fährt die DNA-Polymerase auch immer nur in eine Richtung, nämlich von 5´ nach 3´ (notiert als 5´➝3´)*. Diese Fahrtrichtung des DNA-Kopiervorgangs wird durch die biochemischen Eigenschaften der DNA-Polymerase sowie der DNA festgelegt. Stellen Sie sich nun vor, die DNA-Polymerase rutscht aus, vollzieht eine 180-Grad-Wendung, wechselt auf die Gegenspur und setzt dort die Transkription in entgegengesetzter Richtung fort, als wäre nichts geschehen. Dies ist Template Switching – ein hypothetisches Modell zur Erklärung der Existenz von (Stammschleifen in) micro-RNA-Genen. Es sei darauf hingewiesen, dass die Erzeugung eines ganzen micro-RNA-Gens, wie es im Genom vorgefunden wird (Abb. 2), zwei TS-Runden unmittelbar nacheinander erfordert, d. h. zwei Ausrutscher, also zwei Mal Spurwechsel. Die Forscher berichten in PNAS, dass TS bei der DNA-Replikation eine perfekte Basenpaarung für eine Stammstruktur mit einem einzigen Mutationsereignis bilden kann und an der Entstehung von fast 20 für Menschen spezifischen micro-RNA-Genen beteiligt gewesen sein soll – das sind etwa ein Viertel aller neuen humanspezifischen micro-RNA-Gene (Mönttinen et al. 2023). In Abb. 2 wird der ganze Prozess dargestellt.
Die Eingliederung neuer micro -RNAs in die bestehenden regulatorischen Netzwerke ist absolut unwahrscheinlich.
Figure 1. Abb. 2 Während des Prozesses der DNA-Replikation treten an der Replikationsgabel manchmal Fehler auf, die als Template Switching bezeichnet werden. Dabei handelt es sich um Fehler, bei denen die DNA-Polymerase zweimal die Richtung wechselt. Dies führt zu Palindromen. Evolutionsbiologen erhoffen sich durch diesen Prozess eine Erklärung für micro-RNA-Gene. Oben: 1 DNA-Polymerase rutscht in die falsche Spur. 2 DNA-Polymerase fügt B‘➔A‘ hinzu. 3 DNA-Polymerase rutscht zurück in die richtige Spur und fährt in der richtigen Richtung fort. Mitte: Das Ergebnis des Ausrutschens ist ein Palindrom (blauer Pfeil). Unten: In RNA transkribierte Palindrome können Haarnadel-Strukturen ergeben.
Statt einer Handvoll Unterschiede zwischen Menschen und Schimpansen sehen sich Genomforscher mit einer beträchtlichen Informationslücke konfrontiert. Ist es plausibel, dass zufällige Mutationen im Zusammenspiel mit Selektion die 94 genetischen Unikate menschlicher micro-RNA-Gene hervorgebracht haben? Ein großes Problem dabei ist, dass neue micro-RNAs mit anderen ähnlichen Sequenzen interferieren (wechselwirken) können. Die in Tumorzellen beobachtbare abnorme micro-RNA-Expression wird häufig auf Veränderungen der genomischen micro-RNA-Kopienzahl und ihre Position im Genom (Amplifikation*, Deletion* oder Translokation*) zurückgeführt (Peng & Croce 2016). Um neue micro-RNAs erfolgreich einzugliedern, bedarf es einer Reihe aufeinander abgestimmter Mutationen sowie dazu passender Mutationen an genau den richtigen Stellen der mRNAs, die sie nun regulieren sollen. Auch wenn das Rohmaterial für ein neues micro-RNA-Gen von einem einzigen zufälligen TS stammen sollte (Abb. 2), ist es sehr unwahrscheinlich, dass es sofort und ohne Störung in die bestehenden regulatorischen Netzwerke integriert werden kann. Die für die Neuintegrierung im Genom erforderlichen Änderungen hätten unmittelbar nacheinander auftreten und sich zügig in der gesamten menschlichen Population fixieren müssen. Ein absolut unwahrscheinliches Szenario.
Ein Wandel im evolutionären Denken: Saltationismus statt Darwinismus?
Die Feststellung, dass es 94 humanspezifische micro-RNA-Gene gibt, ist von großer Bedeutung, denn jede micro-RNA bindet und reguliert Netzwerke von Dutzenden oder Hunderten von mRNAs (Lewis et al. 2005). Die Evolutionstheoretiker bieten als Erklärung an, dass ein einziges Mutationsereignis eine neuartige micro-RNA erzeugt haben könnte, sodass diese mit einer Vielzahl von mRNAs interagiert und sofort in ein biologisches Netzwerk integrierbar ist. Wie aber soll das durch einen einzigen zufälligen Mutationsprozess erfolgen? Jede der 94 neuen micro-RNAs muss je nach Zelltyp korrekt eingestellt sein. Sie muss ein- und ausgeschaltet werden können, wenn dies erforderlich ist. Eine Vielzahl von Veränderungen hätte im Laufe von höchstens fünf bis sieben Millionen Jahren in der menschlichen Abstammungslinie selektiert und fixiert worden sein müssen. Dies wäre eine gewaltige sprunghafte Veränderung und sie muss zusätzlich zu all den anderen Unterschieden zwischen Schimpansen und Menschen durch die Evolutionstheorie erklärt werden. Wissenschaftliche Hypothesen müssen vernünftig und frei von unerklärten gewaltigen Sprüngen sein. Der Vorschlag, dass micro-RNA-Gene das Ergebnis eines einzigen Mutationsereignisses sind, bedeutet, dass der klassische Darwinismus mit seinen unmerklich kleinen Schritten der Veränderung bei diesem Phänomen versagt. Erklärt man die beobachtete beträchtliche Diskontinuität in den micro-RNA-Genen durch einzelne, sehr unwahrscheinliche genetische Mutationen, entspräche das dem Saltationismus (sprunghafte Evolution), den Darwin und seine Nachfolger ja entschieden ablehnten.
In der Biologie bezeichnet Saltationismus (von lat. saltus = „Sprung“) eine plötzliche und große Änderung von einer Generation zur nächsten, die möglicherweise zu einer einstufigen Artbildung führt. Im Saltationismus – einer Alternative zu Darwins Gradualismus – wird angenommen, dass größere genetische Veränderungen, chromosomale Aberrationen oder Umstrukturierungen zu einer reproduktiven Isolation von Individuen führen und damit rasch neue Arten hervorbringen können. Ursprünglich wurde die abrupte Speziation (Artbildung) von der neodarwinistischen Schule der „modernen Synthese“ der Evolutionstheorie abgelehnt, da große Änderungen mit einem funktionalen Ergebnis weder theoretisch zu erwarten sind noch experimentell nachweisbar waren. Saltationismus gewinnt aber aufgrund neuerer Erkenntnisse der Evolutionsbiologie wieder an Popularität (Theissen 2009).
Das plötzliche Auftreten von micro-RNA-Genen beim Menschen, die bei Menschenaffen nicht vorkommen, kann evolutionstheoretisch nur als Saltation interpretiert werden. Zudem schreiben die Autoren in PNAS, dass „Template-Switching ein relativ häufiger Mechanismus sei, der Rohmaterial für die Evolution liefert und eine nahezu sofortige Neuverdrahtung der genetischen Information und eine schnelle Anpassung an sich verändernde Umgebungen ermöglicht.“
Aus der Sicht dieser Evolutionsbiologen muss die Entstehung neuer micro-RNA-Gene einfach sein, weil es – so ihre Begründung – viele neue micro-RNA-Gene in unserem Genom gibt. Neue Gene direkt durch Template-Switching zu erhalten, wäre demnach also auch kein anspruchsvoller Vorgang! Doch dies ist ein lupenreiner Zirkelschluss. Ob ein Vorgang einfach ist, entscheidet sich daran, wie er funktioniert, nicht daran, ob er oft vorgekommen sein soll. Dass die Entstehung neuer micro-RNA-Gene nicht einfach ist, wird deutlich, wenn man sich ein voll funktionsfähiges, mehrstöckiges Gebäude vorstellt, in dem alle Leitungen, Strom-, Wasser- und Abwasserleitungen, Zu- und Abluftkanäle usw. integriert sind. Nun muss der Bauunternehmer ein Geschoss zwischen den anderen vorhandenen Etagen so einbauen, dass alles ordnungsgemäß in Betrieb bleibt. Genau so muss man die vollständig in das menschliche Genom integrierten neuen micro-RNAs verstehen. Dass dies in unserem Genom ständig geschieht, stellt eine lang gehegte darwinistische Überzeugung auf den Kopf: Natura non facitsaltus. (Die Natur macht keine Sprünge.) In seinem sehr populären Artikel „Evolution and Tinkering“ erläuterte der Genetiker François Jacob die akzeptierte (neodarwinistische) Sichtweise, warum die Natur keine Sprünge macht:
„(N)achdem das Leben in Form eines primitiven, sich selbst reproduzierenden Organismus begonnen hatte, musste die weitere Evolution durch Veränderungen bereits bestehender Verbindungen erfolgen. [...] In Organismen, die so komplex und vernetzt sind wie die, die schon vor langer Zeit lebten, konnte die Schaffung völlig neuer Nukleotidsequenzen für die Produktion neuer Informationen nicht von Bedeutung sein. [S. 1164].” (Gauger 2018)
Mit anderen Worten: Neue Gene müssen aus bereits existierenden Genen entstehen, weil die Wahrscheinlichkeit der Alternative (Neuentstehung) so gering ist, dass sie ausgeschlossen werden kann. Deshalb ist die Entdeckung von Waisengenen, insbesondere die der micro-RNA-Gene, so problematisch. Und mit gerade einmal 20 micro-RNA-Genen, die mit einem Saltationsvorgang „erklärt“ werden sollten, bleiben die meisten von ihnen (aktuell 74) immer noch Waisen, die einer Erklärung durch Evolution entgegenstehen.
Glossar
5‘➔3‘: In einer Nukleinsäure (DNA oder RNA) ist die Hydroxylgruppe am 3. Kohlenstoffatom (= 3‘) einer Nukleobase mit der Phosphatgruppe der nächsten Base verbunden. Daher wird die Orientierung eines Nukleinsäurestrangs mit 5‘ und 3‘ bezeichnet. Die DNA-Polymerasen bewegen sich immer von 5‘ zu 3‘, kurz 5‘➔3‘.
Amplifikation: Gewinn von Nukleotiden durch Vervielfältigung einer bestehenden Gensequenz (DNA)
Deletion: Verlust von Nukleotiden in der DNA.
Replikation: die identische Verdopplung des Erbguts (DNA)
RNA: Ribonukleinsäure, eine Nukleinsäure, die in allen lebenden Zellen vorkommt. Ihre Hauptaufgabe besteht darin, als Bote zu fungieren, der die Anweisungen der DNA zur Steuerung der Proteinsynthese weiterleitet. In einigen Viren trägt eher die RNA als die DNA die genetische Information. Zunehmend wird festgestellt, dass nicht-codierende RNA, wie z. B. die micro-RNA, wichtige regulatorische Funktionen in Zellen hat.
Translokation: eine Veränderung der Position einer DNA-Sequenz (Gen oder anderes genetisches Element) im Genom
Literatur
Fromm B et al. (2015) A uniform system for the annotation of human microRNA genes and the evolution of the human microRNAome. Annu. Rev. Genet. 23, 213–242.
Gauger A (2018) About Orphan Genes – What’s the Big Problem for Evolution?, https://evolutionnews.org/2018/11/about-orphan-genes-whats-the-big-problem-for-evolution/, vom 11.06.2018.
Lewis BP et al. (2005) Conserved seed pairing, often flanked by adenosines, indicates that thousands of human genes are MicroRNA target, Cell 120, 15–20.
Mönttinen HAM et al. (2022) Template switching in DNA replication can create and maintain RNA hairpins. PNAS 119 (4), e2107005119.
Mönttinen HAM et al. (2023) Generation of de novo miRNAs from template switching during DNA replication. PNA 120 (49), e2310752120.
O’Brien J et al. (2018) Overview of MicroRNA Biogenesis, Mechanisms of Actions, and Circulation. Front. Endocrinol. 9, https://doi.org/10.3389/fendo.2018.00402.
Peng Y & Croce C (2016) The role of MicroRNAs in human cancer. Sig. Transduct. Target. Ther. 1, 15004, https://doi.org/10.1038/sigtrans.2015.4.
Theissen G (2009) Saltational evolution: hopeful monsters are here to stay. Theory Biosci. 128, 43–51.
Eine insbesondere seit Darwin verbreitete Ansicht lautet: „Die Natur macht keine Sprünge.“ Mit Hilfe neuartiger hochempfindlicher Genomforschungsinstrumente scheint diese Ansicht als falsch erwiesen worden zu sein, denn die Genome aller Organismen enthalten eine beträchtliche Anzahl sogenannter Waisengene (engl. orphan genes). Jede untersuchte Gattung hat 10–30 % solcher de-novo-Gene, also Gene, für die keine Evolutionsgeschichte ermittelt werden konnte. Bei diesen Genen kann es sich um proteincodierende Gene, nicht-codierende RNA-Gene und micro-RNA-Gene handeln. Nach einer neuen Studie können micro-RNA-Gene durch ein einziges genetisches Ereignis, das so genannte Template Switching, entstehen.
Eine insbesondere seit Darwin verbreitete Ansicht lautet: „Die Natur macht keine Sprünge.“ Mit Hilfe neuartiger hochempfindlicher Genomforschungsinstrumente scheint diese Ansicht als falsch erwiesen worden zu sein, denn die Genome aller Organismen enthalten eine beträchtliche Anzahl sogenannter Waisengene (engl. orphan genes). Jede untersuchte Gattung hat 10–30 % solcher de-novo-Gene, also Gene, für die keine Evolutionsgeschichte ermittelt werden konnte. Bei diesen Genen kann es sich um proteincodierende Gene, nicht-codierende RNA-Gene und micro-RNA-Gene handeln. Nach einer neuen Studie können micro-RNA-Gene durch ein einziges genetisches Ereignis, das so genannte Template Switching, entstehen.
Abb. 1 (Introbild) Micro-RNA-Gene befinden sich in der DNA. Sie werden in pri-micro-RNAs umgeschrieben, die enzymatisch zu pre-micro-RNAs verarbeitet werden. Diese wiederum werden enzymatisch zu reifen micro-RNAs von etwa 22 Nukleotiden verarbeitet. Reife micro-RNAs kontrollieren die Expression ganzer biologischer Netzwerke, da sie bis zu mehreren hundert Messenger-RNAs binden und deren Abbau bewirken können.
Micro-RNA
Das erste micro-RNA-Gen wurde 1993 völlig unerwartet im Genom des Spulwurms (Caenorhabditis elegans) entdeckt. Anfangs hielt man dies für einen Einzelfall, also etwas, das nirgendwo sonst in der Natur vorkommt. Als die Biologen aber anfingen, gezielt nach micro-RNA-Genen zu suchen, wurden sie in allen Tier- und Pflanzengruppen fündig, bei Schwämmen, Rädertierchen, Pflanzen, Insekten und Säugern (Fromm et al. 2015). Micro-RNA-Gene werden nicht in Proteine umgeschrieben. Stattdessen codieren sie für kurze RNA-Moleküle, die regulatorische Funktionen erfüllen. Bei micro-RNA handelt es sich um kleine RNA-Moleküle, die üblicherweise nur aus 22 Nukleotiden (RNA-Bausteine) bestehen und die messenger-RNA (mRNA) von proteincodierenden Genen erkennen und an diese binden. Auf diese Weise blockieren sie entweder die Übersetzung der mRNA in Proteine oder markieren die mRNA für die Abbaumaschinerie, damit von dem entsprechenden Protein weniger produziert werden kann. In beiden Fällen kommt es zu einer verminderten Produktion des betreffenden Proteins. In der Regel erkennt jede einzelne micro-RNA Hunderte von verschiedenen mRNAs, wodurch die Aktivität von umfangreichen genetischen Programmen gesteuert werden kann. Der Protein-Output von etwa 60 Prozent aller menschlichen Gene wird durch micro-RNAs gesteuert. Micro-RNAs werden auf verschiedene Weise produziert, aber in der Regel werden sie von bestimmten Genen codiert (O‘Brien et al. 2018).
Ein micro-RNA-Gen hat eine leicht erkennbare Struktur, da innerhalb der entsprechenden DNA-Sequenz ein Palindrom vorhanden ist. Ein Palindrom (wie das Wort „Lagerregal“; das Wort kann vorwärts und rückwärts gelesen werden) besteht aus zwei eng beieinander liegenden, benachbarten invertierten Wiederholungen, die intern miteinander durch Basenpaarung eine Haarnadel-Struktur (oder Stammschleife) bilden (Abb. 1). Palindrome in der DNA sind keine Seltenheit und haben oft wichtige biologische Funktionen, da die Schleifen, die sie in DNA-Sequenzen verursachen, oft als Andockstellen für regulatorische Proteine dienen. Gene, die für micro-RNA-Moleküle codieren, sind genauso Bestandteile des menschlichen Genoms wie Gene, die für Proteine codieren. Zellen stellen micro-RNA in einem Prozess her, der den ersten Schritten der Proteinsynthese ähnelt. Das micro-RNA-Gen wird aktiviert, indem der DNA-Strang von einer Transkriptase (Enzym) geöffnet wird. Anschließend wird das Gen in RNA umgeschrieben (Transkription).
Beim Menschen gibt es 94 einzigartige micro -RNA-Gene „ohne Evolutionsgeschichte“.
Es ist immer noch unklar, wie viele micro-RNA-Gene im menschlichen Genom vorhanden sind. Verschiedene Datenbanken geben eine unterschiedliche Anzahl von micro-RNA-Genen an, bis hin zu mehreren Tausend. Jüngste Analysen mit modernsten Techniken bestätigen 567 micro-RNA-Gene im menschlichen Genom, von denen 94 nur beim Menschen vorkommen (https://mirgenedb.org/browse/hsa , am 25.01.2024). Bei Letzteren handelt es sich also um sogenannte Orphan-Gene (Waisengene), d. h. Gene, die nur bei einer bestimmten Art vorkommen und bei denen es keine Hinweise gibt, wie sie im Sinne einer evolutionären Entwicklungsgeschichte interpretiert werden könnten. Dies ist für Evolutionstheoretiker sehr problematisch, denn woher kommen neue Gene, die keine evolutionäre Geschichte haben? In einem kürzlich in der US-amerikanischen Wissenschaftszeitschrift PNAS erschienenen Artikel wird postuliert, dass sie in einem Mutationsprozess namens „Template Switching“ gebildet werden können, der gelegentlich während der DNA-Replikation auftritt (Mönttinen et al. 2023).
Was ist „Template Switching “?
Template Switching (TS; deutsch: Vorlagenwechsel) wird häufig zur Erklärung der Bildung komplexer neuer Haarnadelstrukturen in Genomen herangezogen (Mönttinen et al. 2022). Um zu verstehen, was mit TS gemeint ist, kann man sich die doppelsträngige DNA wie eine zweispurige Straße vorstellen, die in beide Richtungen befahren werden kann – aber immer und nur auf der rechten Seite befahren werden darf, wie es die StVO fordert. Bei der Replikation* der DNA fährt die DNA-Polymerase auch immer nur in eine Richtung, nämlich von 5´ nach 3´ (notiert als 5´➝3´)*. Diese Fahrtrichtung des DNA-Kopiervorgangs wird durch die biochemischen Eigenschaften der DNA-Polymerase sowie der DNA festgelegt. Stellen Sie sich nun vor, die DNA-Polymerase rutscht aus, vollzieht eine 180-Grad-Wendung, wechselt auf die Gegenspur und setzt dort die Transkription in entgegengesetzter Richtung fort, als wäre nichts geschehen. Dies ist Template Switching – ein hypothetisches Modell zur Erklärung der Existenz von (Stammschleifen in) micro-RNA-Genen. Es sei darauf hingewiesen, dass die Erzeugung eines ganzen micro-RNA-Gens, wie es im Genom vorgefunden wird (Abb. 2), zwei TS-Runden unmittelbar nacheinander erfordert, d. h. zwei Ausrutscher, also zwei Mal Spurwechsel. Die Forscher berichten in PNAS, dass TS bei der DNA-Replikation eine perfekte Basenpaarung für eine Stammstruktur mit einem einzigen Mutationsereignis bilden kann und an der Entstehung von fast 20 für Menschen spezifischen micro-RNA-Genen beteiligt gewesen sein soll – das sind etwa ein Viertel aller neuen humanspezifischen micro-RNA-Gene (Mönttinen et al. 2023). In Abb. 2 wird der ganze Prozess dargestellt.
Die Eingliederung neuer micro -RNAs in die bestehenden regulatorischen Netzwerke ist absolut unwahrscheinlich.
Figure 1. Abb. 2 Während des Prozesses der DNA-Replikation treten an der Replikationsgabel manchmal Fehler auf, die als Template Switching bezeichnet werden. Dabei handelt es sich um Fehler, bei denen die DNA-Polymerase zweimal die Richtung wechselt. Dies führt zu Palindromen. Evolutionsbiologen erhoffen sich durch diesen Prozess eine Erklärung für micro-RNA-Gene. Oben: 1 DNA-Polymerase rutscht in die falsche Spur. 2 DNA-Polymerase fügt B‘➔A‘ hinzu. 3 DNA-Polymerase rutscht zurück in die richtige Spur und fährt in der richtigen Richtung fort. Mitte: Das Ergebnis des Ausrutschens ist ein Palindrom (blauer Pfeil). Unten: In RNA transkribierte Palindrome können Haarnadel-Strukturen ergeben.
Statt einer Handvoll Unterschiede zwischen Menschen und Schimpansen sehen sich Genomforscher mit einer beträchtlichen Informationslücke konfrontiert. Ist es plausibel, dass zufällige Mutationen im Zusammenspiel mit Selektion die 94 genetischen Unikate menschlicher micro-RNA-Gene hervorgebracht haben? Ein großes Problem dabei ist, dass neue micro-RNAs mit anderen ähnlichen Sequenzen interferieren (wechselwirken) können. Die in Tumorzellen beobachtbare abnorme micro-RNA-Expression wird häufig auf Veränderungen der genomischen micro-RNA-Kopienzahl und ihre Position im Genom (Amplifikation*, Deletion* oder Translokation*) zurückgeführt (Peng & Croce 2016). Um neue micro-RNAs erfolgreich einzugliedern, bedarf es einer Reihe aufeinander abgestimmter Mutationen sowie dazu passender Mutationen an genau den richtigen Stellen der mRNAs, die sie nun regulieren sollen. Auch wenn das Rohmaterial für ein neues micro-RNA-Gen von einem einzigen zufälligen TS stammen sollte (Abb. 2), ist es sehr unwahrscheinlich, dass es sofort und ohne Störung in die bestehenden regulatorischen Netzwerke integriert werden kann. Die für die Neuintegrierung im Genom erforderlichen Änderungen hätten unmittelbar nacheinander auftreten und sich zügig in der gesamten menschlichen Population fixieren müssen. Ein absolut unwahrscheinliches Szenario.
Ein Wandel im evolutionären Denken: Saltationismus statt Darwinismus?
Die Feststellung, dass es 94 humanspezifische micro-RNA-Gene gibt, ist von großer Bedeutung, denn jede micro-RNA bindet und reguliert Netzwerke von Dutzenden oder Hunderten von mRNAs (Lewis et al. 2005). Die Evolutionstheoretiker bieten als Erklärung an, dass ein einziges Mutationsereignis eine neuartige micro-RNA erzeugt haben könnte, sodass diese mit einer Vielzahl von mRNAs interagiert und sofort in ein biologisches Netzwerk integrierbar ist. Wie aber soll das durch einen einzigen zufälligen Mutationsprozess erfolgen? Jede der 94 neuen micro-RNAs muss je nach Zelltyp korrekt eingestellt sein. Sie muss ein- und ausgeschaltet werden können, wenn dies erforderlich ist. Eine Vielzahl von Veränderungen hätte im Laufe von höchstens fünf bis sieben Millionen Jahren in der menschlichen Abstammungslinie selektiert und fixiert worden sein müssen. Dies wäre eine gewaltige sprunghafte Veränderung und sie muss zusätzlich zu all den anderen Unterschieden zwischen Schimpansen und Menschen durch die Evolutionstheorie erklärt werden. Wissenschaftliche Hypothesen müssen vernünftig und frei von unerklärten gewaltigen Sprüngen sein. Der Vorschlag, dass micro-RNA-Gene das Ergebnis eines einzigen Mutationsereignisses sind, bedeutet, dass der klassische Darwinismus mit seinen unmerklich kleinen Schritten der Veränderung bei diesem Phänomen versagt. Erklärt man die beobachtete beträchtliche Diskontinuität in den micro-RNA-Genen durch einzelne, sehr unwahrscheinliche genetische Mutationen, entspräche das dem Saltationismus (sprunghafte Evolution), den Darwin und seine Nachfolger ja entschieden ablehnten.
In der Biologie bezeichnet Saltationismus (von lat. saltus = „Sprung“) eine plötzliche und große Änderung von einer Generation zur nächsten, die möglicherweise zu einer einstufigen Artbildung führt. Im Saltationismus – einer Alternative zu Darwins Gradualismus – wird angenommen, dass größere genetische Veränderungen, chromosomale Aberrationen oder Umstrukturierungen zu einer reproduktiven Isolation von Individuen führen und damit rasch neue Arten hervorbringen können. Ursprünglich wurde die abrupte Speziation (Artbildung) von der neodarwinistischen Schule der „modernen Synthese“ der Evolutionstheorie abgelehnt, da große Änderungen mit einem funktionalen Ergebnis weder theoretisch zu erwarten sind noch experimentell nachweisbar waren. Saltationismus gewinnt aber aufgrund neuerer Erkenntnisse der Evolutionsbiologie wieder an Popularität (Theissen 2009).
Das plötzliche Auftreten von micro-RNA-Genen beim Menschen, die bei Menschenaffen nicht vorkommen, kann evolutionstheoretisch nur als Saltation interpretiert werden. Zudem schreiben die Autoren in PNAS, dass „Template-Switching ein relativ häufiger Mechanismus sei, der Rohmaterial für die Evolution liefert und eine nahezu sofortige Neuverdrahtung der genetischen Information und eine schnelle Anpassung an sich verändernde Umgebungen ermöglicht.“
Aus der Sicht dieser Evolutionsbiologen muss die Entstehung neuer micro-RNA-Gene einfach sein, weil es – so ihre Begründung – viele neue micro-RNA-Gene in unserem Genom gibt. Neue Gene direkt durch Template-Switching zu erhalten, wäre demnach also auch kein anspruchsvoller Vorgang! Doch dies ist ein lupenreiner Zirkelschluss. Ob ein Vorgang einfach ist, entscheidet sich daran, wie er funktioniert, nicht daran, ob er oft vorgekommen sein soll. Dass die Entstehung neuer micro-RNA-Gene nicht einfach ist, wird deutlich, wenn man sich ein voll funktionsfähiges, mehrstöckiges Gebäude vorstellt, in dem alle Leitungen, Strom-, Wasser- und Abwasserleitungen, Zu- und Abluftkanäle usw. integriert sind. Nun muss der Bauunternehmer ein Geschoss zwischen den anderen vorhandenen Etagen so einbauen, dass alles ordnungsgemäß in Betrieb bleibt. Genau so muss man die vollständig in das menschliche Genom integrierten neuen micro-RNAs verstehen. Dass dies in unserem Genom ständig geschieht, stellt eine lang gehegte darwinistische Überzeugung auf den Kopf: Natura non facitsaltus. (Die Natur macht keine Sprünge.) In seinem sehr populären Artikel „Evolution and Tinkering“ erläuterte der Genetiker François Jacob die akzeptierte (neodarwinistische) Sichtweise, warum die Natur keine Sprünge macht:
„(N)achdem das Leben in Form eines primitiven, sich selbst reproduzierenden Organismus begonnen hatte, musste die weitere Evolution durch Veränderungen bereits bestehender Verbindungen erfolgen. [...] In Organismen, die so komplex und vernetzt sind wie die, die schon vor langer Zeit lebten, konnte die Schaffung völlig neuer Nukleotidsequenzen für die Produktion neuer Informationen nicht von Bedeutung sein. [S. 1164].” (Gauger 2018)
Mit anderen Worten: Neue Gene müssen aus bereits existierenden Genen entstehen, weil die Wahrscheinlichkeit der Alternative (Neuentstehung) so gering ist, dass sie ausgeschlossen werden kann. Deshalb ist die Entdeckung von Waisengenen, insbesondere die der micro-RNA-Gene, so problematisch. Und mit gerade einmal 20 micro-RNA-Genen, die mit einem Saltationsvorgang „erklärt“ werden sollten, bleiben die meisten von ihnen (aktuell 74) immer noch Waisen, die einer Erklärung durch Evolution entgegenstehen.
Glossar
5‘➔3‘: In einer Nukleinsäure (DNA oder RNA) ist die Hydroxylgruppe am 3. Kohlenstoffatom (= 3‘) einer Nukleobase mit der Phosphatgruppe der nächsten Base verbunden. Daher wird die Orientierung eines Nukleinsäurestrangs mit 5‘ und 3‘ bezeichnet. Die DNA-Polymerasen bewegen sich immer von 5‘ zu 3‘, kurz 5‘➔3‘.
Amplifikation: Gewinn von Nukleotiden durch Vervielfältigung einer bestehenden Gensequenz (DNA)
Deletion: Verlust von Nukleotiden in der DNA.
Replikation: die identische Verdopplung des Erbguts (DNA)
RNA: Ribonukleinsäure, eine Nukleinsäure, die in allen lebenden Zellen vorkommt. Ihre Hauptaufgabe besteht darin, als Bote zu fungieren, der die Anweisungen der DNA zur Steuerung der Proteinsynthese weiterleitet. In einigen Viren trägt eher die RNA als die DNA die genetische Information. Zunehmend wird festgestellt, dass nicht-codierende RNA, wie z. B. die micro-RNA, wichtige regulatorische Funktionen in Zellen hat.
Translokation: eine Veränderung der Position einer DNA-Sequenz (Gen oder anderes genetisches Element) im Genom
Literatur
Fromm B et al. (2015) A uniform system for the annotation of human microRNA genes and the evolution of the human microRNAome. Annu. Rev. Genet. 23, 213–242.
Gauger A (2018) About Orphan Genes – What’s the Big Problem for Evolution?, https://evolutionnews.org/2018/11/about-orphan-genes-whats-the-big-problem-for-evolution/, vom 11.06.2018.
Lewis BP et al. (2005) Conserved seed pairing, often flanked by adenosines, indicates that thousands of human genes are MicroRNA target, Cell 120, 15–20.
Mönttinen HAM et al. (2022) Template switching in DNA replication can create and maintain RNA hairpins. PNAS 119 (4), e2107005119.
Mönttinen HAM et al. (2023) Generation of de novo miRNAs from template switching during DNA replication. PNA 120 (49), e2310752120.
O’Brien J et al. (2018) Overview of MicroRNA Biogenesis, Mechanisms of Actions, and Circulation. Front. Endocrinol. 9, https://doi.org/10.3389/fendo.2018.00402.
Peng Y & Croce C (2016) The role of MicroRNAs in human cancer. Sig. Transduct. Target. Ther. 1, 15004, https://doi.org/10.1038/sigtrans.2015.4.
Theissen G (2009) Saltational evolution: hopeful monsters are here to stay. Theory Biosci. 128, 43–51.
