Wie die DNA ständig entknotet wird
Downloads
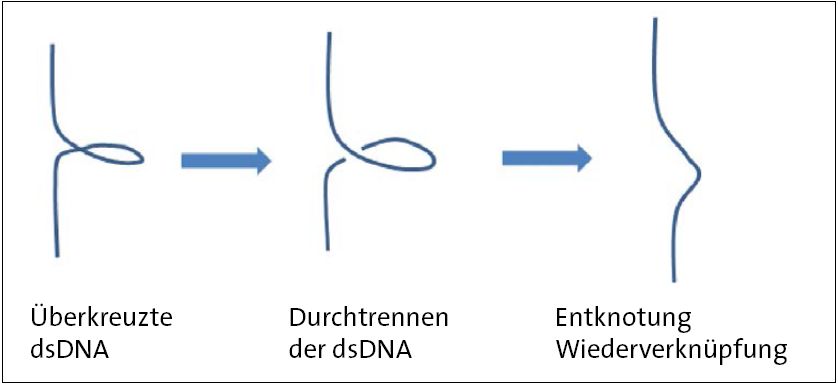
Abb. 1 (Introbild) Schematische Darstellung der Wirkung von Topoisomerasen. Die Doppelstrang-DNA (dsDNA) liegt zunächst überkreuzt vor. Die Topoisomerase trennt an einer Stelle den Strang durch und führt anschließend den anderen Strangteil durch die „Lücke“. Nach der Durchführung wird die dsDNA wieder verknüpft und die übergeordnete Schleife entspannt.
Kaum jemandem dürfte die Beobachtung entgangen sein, dass helixförmige Telefonkabel sich mit der Zeit an einigen Stellen entwinden oder beim unwillkürlichen Drehen des Hörers verwinden, sodass übergeordnete Schleifen entstehen. Durch gezieltes Rotieren des Hörers in einer bestimmten Richtung können die Verdrillungen wieder rückgängig gemacht werden – von selbst lösen sie sich aber nicht.
Ein vergleichbarer Sachverhalt begegnet uns bei der Betrachtung von Erbgutmolekülen. Im Unterschied zu Telefonkabeln ist die DNA jedoch eine Doppelhelix – ein aus zwei Strängen bestehendes spiralförmiges Kettenmolekül. Es enthält die für die Proteinbiosynthese erforderliche Information, die von bestimmten Enzymen unter Entwinden und erneutem Verwinden der Doppelhelix abgelesen wird. Beim Entwinden der DNA kommt es zum Aufbau einer Torsionsspannung – analog zum verdrehten Telefonkabel – und folglich zur Bildung übergeordneter Schleifen in benachbarten Bereichen der Replikationsblase (wo das Ablesen der DNA stattfindet). Solche Schleifen werden auch als „supercoils“ bezeichnet und ihre Auflösung stellte schon seit über vierzig Jahren ein Rätsel in der molekularbiologischen Forschung dar. Supercoils müssen schnell aufgelöst werden, da es anderenfalls zur Bildung von Knoten kommen kann, was für den Ablesevorgang (Transkription) und damit für die gesamte Zelle fatal wäre (Deibler et al. 2007).
Brown und Cozzarelli schlugen bereits im Jahr 1979 aufgrund von Untersuchungen an E.-coli-Bakterien vor, dass als Topoisomerasen bezeichnete Enzyme für das Verhindern der Knotenbildung zuständig sind. Demnach soll das Enzym Gyrase die übergeordneten Schleifen der DNA auflösen. Sie beschrieben damals auch schon einen hypothetischen Mechanismus: Die Gyrase erkennt DNA-Überkreuzungen, schneidet einen Doppelstrang durch, führt den anderen Strangteil durch die Schnittstelle und verschließt diese anschließend wieder. Auf diese Weise wird die Anordnung (Topologie) der übergeordneten Schleife in der DNA spiegelbildlich umgekehrt, sodass die eingeführte Verdrehung der DNA wieder korrigiert wird. Dadurch wird die Knotenbildung verhindert.
Topoisomerasen kommen in allen Domänen des Lebens vor und sind hinsichtlich ihrer Struktur und Funktionsweise recht ähnlich (Reece & Maxwell 1991). Typischerweise bestehen diese Enzyme je nach Organismus aus ca. 600–900 Aminosäuren und zwei Untereinheiten. Damit gehören Topoisomerasen zu den größeren und komplexeren Proteinen. An der Oberfläche, welche die DNA bindet, befinden sich viele positiv geladene Aminosäuren. Dies fördert die Interaktion mit der vielfach negativ geladenen DNA (Cabral et al. 1997). Die Spaltung und erneute Verknüpfung des DNA-Strangs erfolgt unter Verbrauch von ATP – der „Energiewährung“ in Organsimen. Die Auflösung von DNA-Schleifen erfolgt demnach unter Energieverbrauch.
Trotz intensiver Forschungsarbeit konnte der detaillierte Mechanismus der Topoisomerasen lange Zeit nicht beschrieben werden. Erst vor Kurzem ist es zwei kooperierenden Forschungsgruppen gelungen, die Vermutung von Brown und Cozzarelli experimentell zu bestätigen. Mit Hilfe einer relativ neuen Analysenmethode, der Cryoelektronenspektroskopie, konnten die Forscher um Vayssières Schnappschüsse verschiedener Stadien der durch die Gyrase vermittelten Auflösung der DNA-Verdrehung festhalten (vgl. Abb. 1).
Abgesehen von ihren staunenswerten Eigenschaften stellen Topoisomerasen in mehrerer Hinsicht ein schwerwiegendes Problem für Evolutionstheorien dar. Vayssières und andere Autoren schreiben, dass Topoisomerasen in hohem Maße „konserviert“ seien, womit eine sehr geringe Änderung im Zuge der vermeintlich evolutionären Naturgeschichte gemeint ist. Damit stellt sich jedoch die Frage nach ihrer erstmaligen Entstehung. Aufgrund ihrer überaus hohen Komplexität bezüglich Aufbau und Funktionsweise dürfte eine schrittweise Entwicklung alles andere als naheliegend sein. Des Weiteren ist der Umstand, dass das Erbgut ohne diese Enzyme nicht lange intakt bleibt, ähnlich gravierend wie die kritische Rolle von Reparaturenzymen, die zahlreiche Schäden durch reaktive Moleküle beheben (Schmidtgall 2024). Die DNA wird nicht nur ständig repariert, sie wird auch ständig entknotet.
Zudem müssen Topoisomerasen aufzulösende Schleifen auf sehr präzise Weise erkennen können, da sie anderenfalls Verdrillungen einführen würden statt sie zu lösen. Dies würde aber die Verknotung der DNA noch verstärken. Ein „suboptimales“ Design evolutiver Vorstufen von Topoisomerasen wäre daher fatal. Das spricht sehr stark für eine ganzheitliche Lebensentstehung, die nur aus einer Schöpfungsperspektive verständlich ist.
[Brown PO & Cozzarelli NR (1979) A sign inversion mechanism for enzymatic supercoiling of DNA. Science 206, 1081–1083 • Cabral JH et al. (1997) Crystal structure of the breakage-reunion domain of DNA gyrase. Nature 388, 903–906 • Deibler RW et al. (2007) Hin-mediated DNA knotting and recombining promote replicon dysfunction and mutation. BMC Mol. Biol. 8, 44 • Reece RJ & Maxwell A (1991) DNA Gyrase: structure and function. Crit. Rev. Biochem. Mol. Biol. 26, 335–375 • Schmidtgall B (2024) Reparaturmechanismen in der Zelle. Stud. Integr. J. 31, 29–38 • Vayssières M et al. (2024) Structural basis of DNA crossover capture by Escherichia coli DNA gyrase. Science 384, 227–232]
Abb. 1 (Introbild) Schematische Darstellung der Wirkung von Topoisomerasen. Die Doppelstrang-DNA (dsDNA) liegt zunächst überkreuzt vor. Die Topoisomerase trennt an einer Stelle den Strang durch und führt anschließend den anderen Strangteil durch die „Lücke“. Nach der Durchführung wird die dsDNA wieder verknüpft und die übergeordnete Schleife entspannt.
Kaum jemandem dürfte die Beobachtung entgangen sein, dass helixförmige Telefonkabel sich mit der Zeit an einigen Stellen entwinden oder beim unwillkürlichen Drehen des Hörers verwinden, sodass übergeordnete Schleifen entstehen. Durch gezieltes Rotieren des Hörers in einer bestimmten Richtung können die Verdrillungen wieder rückgängig gemacht werden – von selbst lösen sie sich aber nicht.
Ein vergleichbarer Sachverhalt begegnet uns bei der Betrachtung von Erbgutmolekülen. Im Unterschied zu Telefonkabeln ist die DNA jedoch eine Doppelhelix – ein aus zwei Strängen bestehendes spiralförmiges Kettenmolekül. Es enthält die für die Proteinbiosynthese erforderliche Information, die von bestimmten Enzymen unter Entwinden und erneutem Verwinden der Doppelhelix abgelesen wird. Beim Entwinden der DNA kommt es zum Aufbau einer Torsionsspannung – analog zum verdrehten Telefonkabel – und folglich zur Bildung übergeordneter Schleifen in benachbarten Bereichen der Replikationsblase (wo das Ablesen der DNA stattfindet). Solche Schleifen werden auch als „supercoils“ bezeichnet und ihre Auflösung stellte schon seit über vierzig Jahren ein Rätsel in der molekularbiologischen Forschung dar. Supercoils müssen schnell aufgelöst werden, da es anderenfalls zur Bildung von Knoten kommen kann, was für den Ablesevorgang (Transkription) und damit für die gesamte Zelle fatal wäre (Deibler et al. 2007).
Brown und Cozzarelli schlugen bereits im Jahr 1979 aufgrund von Untersuchungen an E.-coli-Bakterien vor, dass als Topoisomerasen bezeichnete Enzyme für das Verhindern der Knotenbildung zuständig sind. Demnach soll das Enzym Gyrase die übergeordneten Schleifen der DNA auflösen. Sie beschrieben damals auch schon einen hypothetischen Mechanismus: Die Gyrase erkennt DNA-Überkreuzungen, schneidet einen Doppelstrang durch, führt den anderen Strangteil durch die Schnittstelle und verschließt diese anschließend wieder. Auf diese Weise wird die Anordnung (Topologie) der übergeordneten Schleife in der DNA spiegelbildlich umgekehrt, sodass die eingeführte Verdrehung der DNA wieder korrigiert wird. Dadurch wird die Knotenbildung verhindert.
Topoisomerasen kommen in allen Domänen des Lebens vor und sind hinsichtlich ihrer Struktur und Funktionsweise recht ähnlich (Reece & Maxwell 1991). Typischerweise bestehen diese Enzyme je nach Organismus aus ca. 600–900 Aminosäuren und zwei Untereinheiten. Damit gehören Topoisomerasen zu den größeren und komplexeren Proteinen. An der Oberfläche, welche die DNA bindet, befinden sich viele positiv geladene Aminosäuren. Dies fördert die Interaktion mit der vielfach negativ geladenen DNA (Cabral et al. 1997). Die Spaltung und erneute Verknüpfung des DNA-Strangs erfolgt unter Verbrauch von ATP – der „Energiewährung“ in Organsimen. Die Auflösung von DNA-Schleifen erfolgt demnach unter Energieverbrauch.
Trotz intensiver Forschungsarbeit konnte der detaillierte Mechanismus der Topoisomerasen lange Zeit nicht beschrieben werden. Erst vor Kurzem ist es zwei kooperierenden Forschungsgruppen gelungen, die Vermutung von Brown und Cozzarelli experimentell zu bestätigen. Mit Hilfe einer relativ neuen Analysenmethode, der Cryoelektronenspektroskopie, konnten die Forscher um Vayssières Schnappschüsse verschiedener Stadien der durch die Gyrase vermittelten Auflösung der DNA-Verdrehung festhalten (vgl. Abb. 1).
Abgesehen von ihren staunenswerten Eigenschaften stellen Topoisomerasen in mehrerer Hinsicht ein schwerwiegendes Problem für Evolutionstheorien dar. Vayssières und andere Autoren schreiben, dass Topoisomerasen in hohem Maße „konserviert“ seien, womit eine sehr geringe Änderung im Zuge der vermeintlich evolutionären Naturgeschichte gemeint ist. Damit stellt sich jedoch die Frage nach ihrer erstmaligen Entstehung. Aufgrund ihrer überaus hohen Komplexität bezüglich Aufbau und Funktionsweise dürfte eine schrittweise Entwicklung alles andere als naheliegend sein. Des Weiteren ist der Umstand, dass das Erbgut ohne diese Enzyme nicht lange intakt bleibt, ähnlich gravierend wie die kritische Rolle von Reparaturenzymen, die zahlreiche Schäden durch reaktive Moleküle beheben (Schmidtgall 2024). Die DNA wird nicht nur ständig repariert, sie wird auch ständig entknotet.
Zudem müssen Topoisomerasen aufzulösende Schleifen auf sehr präzise Weise erkennen können, da sie anderenfalls Verdrillungen einführen würden statt sie zu lösen. Dies würde aber die Verknotung der DNA noch verstärken. Ein „suboptimales“ Design evolutiver Vorstufen von Topoisomerasen wäre daher fatal. Das spricht sehr stark für eine ganzheitliche Lebensentstehung, die nur aus einer Schöpfungsperspektive verständlich ist.
[Brown PO & Cozzarelli NR (1979) A sign inversion mechanism for enzymatic supercoiling of DNA. Science 206, 1081–1083 • Cabral JH et al. (1997) Crystal structure of the breakage-reunion domain of DNA gyrase. Nature 388, 903–906 • Deibler RW et al. (2007) Hin-mediated DNA knotting and recombining promote replicon dysfunction and mutation. BMC Mol. Biol. 8, 44 • Reece RJ & Maxwell A (1991) DNA Gyrase: structure and function. Crit. Rev. Biochem. Mol. Biol. 26, 335–375 • Schmidtgall B (2024) Reparaturmechanismen in der Zelle. Stud. Integr. J. 31, 29–38 • Vayssières M et al. (2024) Structural basis of DNA crossover capture by Escherichia coli DNA gyrase. Science 384, 227–232]
